[i=s] 本帖最后由 galaxy 于 2025-3-5 22:06 编辑 [/i]
Seurat报错 Error in fixupDN.if.valid(value, x@Dim) :length of Dimnames[[1]] (54575) is not equal to Dim[1] (54574)
在我们读取公共数据库的10X文件时,可能会出现以下报错:(图一)
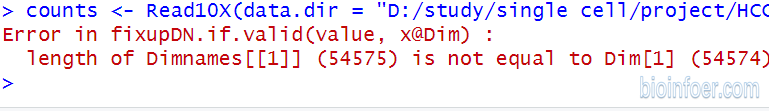
(图一)
原因:
可见features.tsv有54575行,比矩阵的基因多了一个,这大概率是上传者给feature文件添加了表头,我们打开看看(图二),果然,不仅多了1行表头,还多了后面5列10X官网示例文件中没有的注释信息(10X官网的文件只有前两列且没有表头)
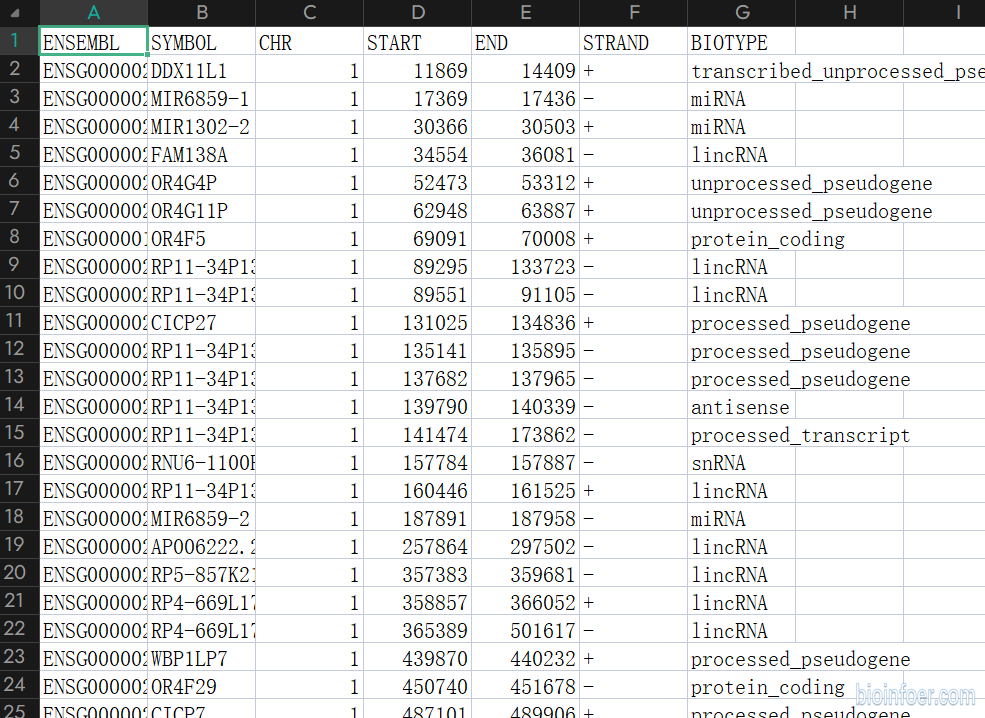
(图二)
解决方法:
删掉多余的行和列,变成10X官网格式,再压缩成GZ格式,此时文件名应为“features.tsv.gz”
注意
1:文件名不对也不行哦。
2:除了前两列,后面的列也需要删除,否则读进去的文件会是一个list,不是一个矩阵,在后续创建seurat对象时会报错
 |Archiver|手机版|小黑屋|bioinfoer
( 萌ICP备20244422号 )
|Archiver|手机版|小黑屋|bioinfoer
( 萌ICP备20244422号 )